Algunos microbios pueden formar películas delgadas llamadas biopelículas. Estas biopelículas les dan una ventaja sobre otros microbios al protegerlos de estreses como la falta de nutrientes o la presencia de sustancias nocivas en el medio ambiente.
por el Laboratorio Nacional Oak Ridge
Los investigadores a menudo se centran en las biopelículas que utilizan los patógenos para resistir a los antibióticos. Sin embargo, algunas biopelículas pueden ser útiles para las plantas y otros organismos hospedadores. En trabajos anteriores, los investigadores encontraron que Pantoea sp. YR343, una bacteria que promueve el crecimiento de las plantas, forma biopelículas robustas a lo largo de la superficie de la raíz de Populus, el género que incluye sauces y álamos. Los científicos saben relativamente poco sobre los mecanismos detrás de la formación de biopelículas en las raíces de las plantas, particularmente a nivel genético. Sin embargo, la investigación ha encontrado que las enzimas llamadas ciclasas de diguanilato son clave para la formación de biopelículas.
Las diguanilato ciclasas se encuentran en muchas especies de bacterias. Estas enzimas controlan múltiples comportamientos, incluida la forma en que las bacterias forman biopelículas, causan enfermedades y se mueven. Esta investigación muestra que una diguanilato ciclasa en particular, DGC2884, opera específicamente durante la formación de biopelículas y cuando las bacterias están cerca de una planta. Esta investigación también identificó genes que podrían estar involucrados en la colonización de raíces , lo que sugiere que la colonización de raíces puede controlarse a nivel genético . Esto ayudará a los microbiólogos y otros investigadores a comprender mejor cómo las bacterias colonizan las superficies de las raíces y cómo la expresión génica puede desempeñar un papel. Los resultados también pueden ayudar a los científicos a estudiar comportamientos similares en microbios importantes para la medicina y la agricultura.
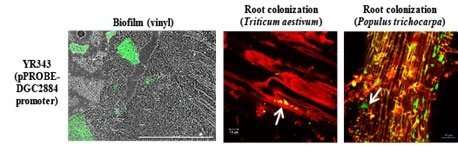
Este estudio utilizó construcciones de promotor-indicador para identificar una diguanilato ciclasa, DGC2884, que se expresa en presencia de una planta. Los investigadores caracterizaron más esta enzima y determinaron que cuando se sobreexpresaba, afectaba la producción de exopolisacáridos, la formación de biopelículas, la motilidad y la formación de películas. También demostraron que el dominio transmembrana N-terminal, así como un sitio activo GGDEF funcional, son necesarios para la actividad de DGC2884. Basado en fenotipos asociados con la sobreexpresión de DGC2884 en Pantoea sp. YR343, los científicos realizaron mutagénesis de transposones para identificar genes que ya no exhibían los fenotipos únicos observados cuando se sobreexpresaba DGC2884. Identificaron 58 genes diferentes con esta pantalla y seleccionaron un subconjunto de mutantes de transposones para una caracterización adicional. Curiosamente las mutaciones que afectan la secreción de tipo VI, así como una nucleósido-difosfato quinasa y un transportador ABC, mostraron aumentos en la colonización, mientras que las mutaciones que afectan la producción de exopolisacáridos dieron como resultado una disminución de la colonización en comparación con el control de tipo salvaje. Además, encontraron que algunos mutantes exhibían diferencias principalmente en los patrones de colonización de raíces, más que en la cantidad de colonización, lo que sugiere que ciertos patrones de colonización de raíces pueden modularse a nivel genético.
La investigación fue publicada en PLOS ONE .
